+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of rabbit Slo1 in complex with gamma1/LRRC26 | |||||||||
 マップデータ マップデータ | Map sharpened by Phenix | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Ion channel (イオンチャネル) / potassium transport / Ion channel (イオンチャネル) / potassium transport /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報monoatomic ion-gated channel activity / monoatomic ion channel complex /  potassium channel activity / endoplasmic reticulum membrane / potassium channel activity / endoplasmic reticulum membrane /  metal ion binding / metal ion binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) | |||||||||
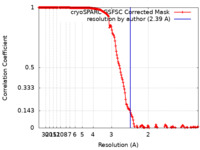
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.39 Å クライオ電子顕微鏡法 / 解像度: 2.39 Å | |||||||||
 データ登録者 データ登録者 | Redhardt M / Raunser S / Raisch T | |||||||||
| 資金援助 |  ドイツ, 1件 ドイツ, 1件
| |||||||||
 引用 引用 |  ジャーナル: FEBS Lett / 年: 2024 ジャーナル: FEBS Lett / 年: 2024タイトル: Cryo-EM structure of the Slo1 potassium channel with the auxiliary γ1 subunit suggests a mechanism for depolarization-independent activation. 著者: Milena Redhardt / Stefan Raunser / Tobias Raisch /  要旨: Mammalian Ca-dependent Slo K channels can stably associate with auxiliary γ subunits which fundamentally alter their behavior. By a so far unknown mechanism, the four γ subunits reduce the need for ...Mammalian Ca-dependent Slo K channels can stably associate with auxiliary γ subunits which fundamentally alter their behavior. By a so far unknown mechanism, the four γ subunits reduce the need for voltage-dependent activation and, thereby, allow Slo to open independently of an action potential. Here, using cryo-EM, we reveal how the transmembrane helix of γ1/LRRC26 binds and presumably stabilizes the activated voltage-sensor domain of Slo1. The activation is further enhanced by an intracellular polybasic stretch which locally changes the charge gradient across the membrane. Our data provide a possible explanation for Slo1 regulation by the four γ subunits and also their different activation efficiencies. This suggests a novel activation mechanism of voltage-gated ion channels by auxiliary subunits. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_19691.map.gz emd_19691.map.gz | 400.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-19691-v30.xml emd-19691-v30.xml emd-19691.xml emd-19691.xml | 21.5 KB 21.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_19691_fsc.xml emd_19691_fsc.xml | 16.9 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_19691.png emd_19691.png | 188 KB | ||
| Filedesc metadata |  emd-19691.cif.gz emd-19691.cif.gz | 6.6 KB | ||
| その他 |  emd_19691_additional_1.map.gz emd_19691_additional_1.map.gz emd_19691_additional_2.map.gz emd_19691_additional_2.map.gz emd_19691_half_map_1.map.gz emd_19691_half_map_1.map.gz emd_19691_half_map_2.map.gz emd_19691_half_map_2.map.gz | 249.7 MB 432.4 MB 475.2 MB 475.2 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-19691 http://ftp.pdbj.org/pub/emdb/structures/EMD-19691 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19691 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19691 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8s3eMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_19691.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_19691.map.gz / 形式: CCP4 / 大きさ: 512 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map sharpened by Phenix | ||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.68 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
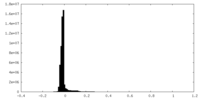
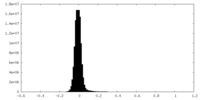
-追加マップ: Unfiltered map from cryoSPARC
| ファイル | emd_19691_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Unfiltered map from cryoSPARC | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
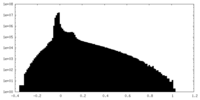
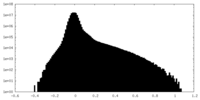
-追加マップ: Map sharpened using DeepEMhancer
| ファイル | emd_19691_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Map sharpened using DeepEMhancer | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
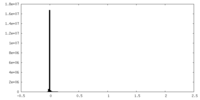
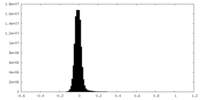
-ハーフマップ: Half map A
| ファイル | emd_19691_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map A | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
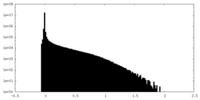
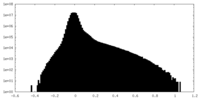
-ハーフマップ: Half map B
| ファイル | emd_19691_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Half map B | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Slo1-gamma1 complex
| 全体 | 名称: Slo1-gamma1 complex |
|---|---|
| 要素 |
|
-超分子 #1: Slo1-gamma1 complex
| 超分子 | 名称: Slo1-gamma1 complex / タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) |
-分子 #1: Calcium-activated potassium channel subunit alpha-1
| 分子 | 名称: Calcium-activated potassium channel subunit alpha-1 / タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) |
| 分子量 | 理論値: 126.029523 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MDALIIPVTM EVPCDSRGQR MWWAFLASSM VTFFGGLFII LLWRTLKYLW TVCCHCGGKA KEAQKINNGS SQADGTLKPV DEKEEAVAA EVGWMTSVKD WAGVMISAQT LTGRVLVVLV FALSIGALVI YFIDSSNPIE SCQNFYKDFT LQIDMAFNVF F LLYFGLRF ...文字列: MDALIIPVTM EVPCDSRGQR MWWAFLASSM VTFFGGLFII LLWRTLKYLW TVCCHCGGKA KEAQKINNGS SQADGTLKPV DEKEEAVAA EVGWMTSVKD WAGVMISAQT LTGRVLVVLV FALSIGALVI YFIDSSNPIE SCQNFYKDFT LQIDMAFNVF F LLYFGLRF IAANDKLWFW LEVNSVVDFF TVPPVFVSVY LNRSWLGLRF LRALRLIQFS EILQFLNILK TSNSIKLVNL LS IFISTWL TAAGFIHLVE NSGDPWENFQ NNQALTYWEC VYLLMVTMST VGYGDVYAKT TLGRLFMVFF ILGGLAMFAS YVP EIIELI GNRKKYGGSY SAVSGRKHIV VCGHITLESV SNFLKDFLHK DRDDVNVEIV FLHNISPNLE LEALFKRHFT QVEF YQGSV LNPHDLARVK IESADACLIL ANKYCADPDA EDASNIMRVI SIKNYHPKIR IITQMLQYHN KAHLLNIPSW NWKEG DDAI CLAELKLGFI AQSCLAQGLS TMLANLFSMR SFIKIEEDTW QKYYLEGVSN EMYTEYLSSA FVGLSFPTVC ELCFVK LKL LMIAIEYKSA NRESRILINP GNHLKIQEGT LGFFIASDAK EVKRAFFYCK ACHDDITDPK RIKKCGCKRL EDEQPST LS PKKKQRNGGM RNSPNSSPKL MRHDPLLIPG NDQIDNMDSN VKKYDSTGMF HWCAPKEIEK VILTRSEAAM TVLSGHVV V CIFGDVSSAL IGLRNLVMPL RASNFHYHEL KHIVFVGSIE YLKREWETLH NFPKVSILPG TPLSRADLRA VNINLCDMC VILSANQNNI DDTSLQDKEC ILASLNIKSM QFDDSIGVLQ ANSQGFTPPG MDRSSPDNSP VHGMLRQPSI TTGVNIPIIT ELVNDTNVQ FLDQDDDDDP DTELYLTQPF ACGTAFAVSV LDSLMSATYF NDNILTLIRT LVTGGATPEL EALIAEENAL R GGYSTPQT LANRDRCRVA QLALLDGPFA DLGDGGCYGD LFCKALKTYN MLCFGIYRLR DAHLSTPSQC TKRYVITNPP YE FELVPTD LIFCLMQFDH NAGQSRASLS HSSHSSQSSS KKSSSVHSIP STANRQNRPK SRESRDKQKY VQEERLLEVL FQ UniProtKB:  Calcium-activated potassium channel subunit alpha-1 Calcium-activated potassium channel subunit alpha-1 |
-分子 #2: Leucine-rich repeat-containing protein 26
| 分子 | 名称: Leucine-rich repeat-containing protein 26 / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Oryctolagus cuniculus (ウサギ) Oryctolagus cuniculus (ウサギ) |
| 分子量 | 理論値: 35.938766 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MRSPSFSSWP PPLLLLLLLH PWQVCAQAPS LATSSGVSGA PDCPEACACA PGGQANCSAL ALSAVPAGLS RRVRALLLDH NRLGSLPPG AFADADALLR LDLRENELRW VHARAFWGLG ALQRLDLSAN RLEALAPGTF GPLRALRTLS LAGNRLARLE P AALGALPL ...文字列: MRSPSFSSWP PPLLLLLLLH PWQVCAQAPS LATSSGVSGA PDCPEACACA PGGQANCSAL ALSAVPAGLS RRVRALLLDH NRLGSLPPG AFADADALLR LDLRENELRW VHARAFWGLG ALQRLDLSAN RLEALAPGTF GPLRALRTLS LAGNRLARLE P AALGALPL LRALSLQDNA LSALSPGLLA GLPALDALRL RGNPWTCDCA LRPLCTWLRR HPRPASEAET PVCVSPGRLA RS PLAAFPD AAFRHCARPL SPRDLAMIYL LGPASFLASL VACLALGSAL TACRARRRRR QRTAAHRPPR RSLDLDPGGP ASP ANAGSP AEAGLGRPLE VLFQ |
-分子 #3: CHOLESTEROL
| 分子 | 名称: CHOLESTEROL / タイプ: ligand / ID: 3 / コピー数: 16 / 式: CLR |
|---|---|
| 分子量 | 理論値: 386.654 Da |
| Chemical component information |  ChemComp-CLR: |
-分子 #4: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 4 / コピー数: 8 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-分子 #5: (4S,7R)-4-HYDROXY-N,N,N-TRIMETHYL-9-OXO-7-[(PALMITOYLOXY)METHYL]-...
| 分子 | 名称: (4S,7R)-4-HYDROXY-N,N,N-TRIMETHYL-9-OXO-7-[(PALMITOYLOXY)METHYL]-3,5,8-TRIOXA-4-PHOSPHAHEXACOSAN-1-AMINIUM 4-OXIDE タイプ: ligand / ID: 5 / コピー数: 36 / 式: 6PL |
|---|---|
| 分子量 | 理論値: 763.1 Da |
| Chemical component information |  ChemComp-6PL: |
-分子 #6: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 6 / コピー数: 4 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-分子 #7: POTASSIUM ION
| 分子 | 名称: POTASSIUM ION / タイプ: ligand / ID: 7 / コピー数: 4 / 式: K |
|---|---|
| 分子量 | 理論値: 39.098 Da |
-分子 #8: water
| 分子 | 名称: water / タイプ: ligand / ID: 8 / コピー数: 13 / 式: HOH |
|---|---|
| 分子量 | 理論値: 18.015 Da |
| Chemical component information |  ChemComp-HOH: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: OTHER / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.2 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.4 µm / 最小 デフォーカス(公称値): 1.2 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 52.3 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー




 Z
Z Y
Y X
X