+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-23858 | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Mouse TRPV3 in cNW11 nanodiscs, open state at 42 degrees Celsius | |||||||||||||||
 マップデータ マップデータ | TRPV3 in cNW11 nanodiscs, open state at 42 degrees Celsius | |||||||||||||||
 試料 試料 |
| |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of hair cycle /  TRPチャネル / response to temperature stimulus / positive regulation of calcium ion import / monoatomic cation channel activity / TRPチャネル / response to temperature stimulus / positive regulation of calcium ion import / monoatomic cation channel activity /  calcium channel activity / monoatomic ion channel activity / calcium channel activity / monoatomic ion channel activity /  receptor complex / receptor complex /  生体膜 / identical protein binding 生体膜 / identical protein binding類似検索 - 分子機能 | |||||||||||||||
| 生物種 |   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) | |||||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.48 Å クライオ電子顕微鏡法 / 解像度: 3.48 Å | |||||||||||||||
 データ登録者 データ登録者 | Nadezhdin KD / Neuberger A / Sobolevsky AI | |||||||||||||||
| 資金援助 |  米国, 4件 米国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2021 ジャーナル: Nat Struct Mol Biol / 年: 2021タイトル: Structural mechanism of heat-induced opening of a temperature-sensitive TRP channel. 著者: Kirill D Nadezhdin / Arthur Neuberger / Yuri A Trofimov / Nikolay A Krylov / Viktor Sinica / Nikita Kupko / Viktorie Vlachova / Eleonora Zakharian / Roman G Efremov / Alexander I Sobolevsky /    要旨: Numerous physiological functions rely on distinguishing temperature through temperature-sensitive transient receptor potential channels (thermo-TRPs). Although the function of thermo-TRPs has been ...Numerous physiological functions rely on distinguishing temperature through temperature-sensitive transient receptor potential channels (thermo-TRPs). Although the function of thermo-TRPs has been studied extensively, structural determination of their heat- and cold-activated states has remained a challenge. Here, we present cryo-EM structures of the nanodisc-reconstituted wild-type mouse TRPV3 in three distinct conformations: closed, heat-activated sensitized and open states. The heat-induced transformations of TRPV3 are accompanied by changes in the secondary structure of the S2-S3 linker and the N and C termini and represent a conformational wave that links these parts of the protein to a lipid occupying the vanilloid binding site. State-dependent differences in the behavior of bound lipids suggest their active role in thermo-TRP temperature-dependent gating. Our structural data, supported by physiological recordings and molecular dynamics simulations, provide an insight for understanding the molecular mechanism of temperature sensing. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_23858.map.gz emd_23858.map.gz | 59.9 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-23858-v30.xml emd-23858-v30.xml emd-23858.xml emd-23858.xml | 17 KB 17 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_23858.png emd_23858.png | 172.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-23858 http://ftp.pdbj.org/pub/emdb/structures/EMD-23858 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23858 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-23858 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_23858.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_23858.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | TRPV3 in cNW11 nanodiscs, open state at 42 degrees Celsius | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 0.87082 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Transient receptor potential cation channel subfamily V member 3
| 全体 | 名称: Transient receptor potential cation channel subfamily V member 3 |
|---|---|
| 要素 |
|
-超分子 #1: Transient receptor potential cation channel subfamily V member 3
| 超分子 | 名称: Transient receptor potential cation channel subfamily V member 3 タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 924.7 KDa |
-分子 #1: Transient receptor potential cation channel subfamily V member 3
| 分子 | 名称: Transient receptor potential cation channel subfamily V member 3 タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 92.630695 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MNAHSKEMAP LMGKRTTAPG GNPVVLTEKR PADLTPTKKS AHFFLEIEGF EPNPTVTKTS PPIFSKPMDS NIRQCLSGNC DDMDSPQSP QDDVTETPSN PNSPSANLAK EEQRQKKKRL KKRIFAAVSE GCVEELRELL QDLQDLCRRR RGLDVPDFLM H KLTASDTG ...文字列: MNAHSKEMAP LMGKRTTAPG GNPVVLTEKR PADLTPTKKS AHFFLEIEGF EPNPTVTKTS PPIFSKPMDS NIRQCLSGNC DDMDSPQSP QDDVTETPSN PNSPSANLAK EEQRQKKKRL KKRIFAAVSE GCVEELRELL QDLQDLCRRR RGLDVPDFLM H KLTASDTG KTCLMKALLN INPNTKEIVR ILLAFAEEND ILDRFINAEY TEEAYEGQTA LNIAIERRQG DITAVLIAAG AD VNAHAKG VFFNPKYQHE GFYFGETPLA LAACTNQPEI VQLLMENEQT DITSQDSRGN NILHALVTVA EDFKTQNDFV KRM YDMILL RSGNWELETM RNNDGLTPLQ LAAKMGKAEI LKYILSREIK EKPLRSLSRK FTDWAYGPVS SSLYDLTNVD TTTD NSVLE IIVYNTNIDN RHEMLTLEPL HTLLHTKWKK FAKYMFFLSF CFYFFYNITL TLVSYYRPRE DEDLPHPLAL THKMS WLQL LGRMFVLIWA TCISVKEGIA IFLLRPSDLQ SILSDAWFHF VFFVQAVLVI LSVFLYLFAY KEYLACLVLA MALGWA NML YYTRGFQSMG MYSVMIQKVI LHDVLKFLFV YILFLLGFGV ALASLIEKCS KDKKDCSSYG SFSDAVLELF KLTIGLG DL NIQQNSTYPI LFLFLLITYV ILTFVLLLNM LIALMGETVE NVSKESERIW RLQRARTILE FEKMLPEWLR SRFRMGEL C KVADEDFRLC LRINEVKWTE WKTHVSFLNE DPGPIRRTAD LNKIQDSSRS NSKTTLYAFD ELDEFPETSV LVPRGSAAA WSHPQFEK |
-分子 #2: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(tri...
| 分子 | 名称: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(trimethylammonio)ethyl phosphate タイプ: ligand / ID: 2 / コピー数: 28 / 式: POV |
|---|---|
| 分子量 | 理論値: 760.076 Da |
| Chemical component information | 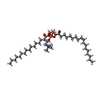 ChemComp-POV: |
-分子 #3: SODIUM ION
| 分子 | 名称: SODIUM ION / タイプ: ligand / ID: 3 / コピー数: 1 |
|---|---|
| 分子量 | 理論値: 22.99 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.0 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 8 構成要素:
| |||||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | TFS KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.0 µm / 最小 デフォーカス(公称値): -0.5 µm Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): -2.0 µm / 最小 デフォーカス(公称値): -0.5 µm |
| 特殊光学系 | エネルギーフィルター - スリット幅: 30 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / デジタル化 - サイズ - 横: 5760 pixel / デジタル化 - サイズ - 縦: 4092 pixel / 撮影したグリッド数: 1 / 実像数: 18667 / 平均露光時間: 2.5 sec. / 平均電子線量: 59.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 粒子像選択 | 選択した数: 6869494 |
|---|---|
| CTF補正 | ソフトウェア - 名称: RELION (ver. 3.1) |
| 初期 角度割当 | タイプ: OTHER / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 3次元分類 | ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 角度割当 | タイプ: OTHER / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.48 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 27805 |
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|---|
| 得られたモデル |  PDB-7mio: |
 ムービー
ムービー コントローラー
コントローラー





















