+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-0882 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | cryo-EM structure of TRPV3 in lipid nanodisc | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  TRP channel (TRPチャネル) / TRP channel (TRPチャネル) /  TRPV family / TRPV family /  TRPV3 / TRPV3 /  nanodisc / nanodisc /  MEMBRANE PROTEIN (膜タンパク質) MEMBRANE PROTEIN (膜タンパク質) | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of hair cycle /  TRPチャネル / response to temperature stimulus / positive regulation of calcium ion import / monoatomic cation channel activity / TRPチャネル / response to temperature stimulus / positive regulation of calcium ion import / monoatomic cation channel activity /  calcium channel activity / monoatomic ion channel activity / calcium channel activity / monoatomic ion channel activity /  receptor complex / receptor complex /  生体膜 / identical protein binding 生体膜 / identical protein binding類似検索 - 分子機能 | |||||||||
| 生物種 |   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.3 Å クライオ電子顕微鏡法 / 解像度: 3.3 Å | |||||||||
 データ登録者 データ登録者 | Shimada H / Kusakizako T | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2020 ジャーナル: Nat Struct Mol Biol / 年: 2020タイトル: The structure of lipid nanodisc-reconstituted TRPV3 reveals the gating mechanism. 著者: Hiroto Shimada / Tsukasa Kusakizako / T H Dung Nguyen / Tomohiro Nishizawa / Tomoya Hino / Makoto Tominaga / Osamu Nureki /  要旨: Transient receptor potential vanilloid subfamily member 3 (TRPV3) is a temperature-sensitive cation channel. Previous cryo-EM analyses of TRPV3 in detergent micelles or amphipol proposed that the ...Transient receptor potential vanilloid subfamily member 3 (TRPV3) is a temperature-sensitive cation channel. Previous cryo-EM analyses of TRPV3 in detergent micelles or amphipol proposed that the lower gate opens by α-to-π helical transitions of the nearby S6 helix. However, it remains unclear how physiological lipids are involved in the TRPV3 activation. Here we determined the apo state structure of mouse (Mus musculus) TRPV3 in a lipid nanodisc at 3.3 Å resolution. The structure revealed that lipids bound to the pore domain stabilize the selectivity filter in the narrow state, suggesting that the selectivity filter of TRPV3 affects cation permeation. When the lower gate is closed in nanodisc-reconstituted TRPV3, the S6 helix adopts the π-helical conformation without agonist- or heat-sensitization, potentially stabilized by putative intra-subunit hydrogen bonds and lipid binding. Our findings provide insights into the lipid-associated gating mechanism of TRPV3. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_0882.map.gz emd_0882.map.gz | 2.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-0882-v30.xml emd-0882-v30.xml emd-0882.xml emd-0882.xml | 15.4 KB 15.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_0882_fsc.xml emd_0882_fsc.xml | 5.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_0882.png emd_0882.png | 116.5 KB | ||
| マスクデータ |  emd_0882_msk_1.map emd_0882_msk_1.map | 15.6 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-0882.cif.gz emd-0882.cif.gz | 5.8 KB | ||
| その他 |  emd_0882_half_map_1.map.gz emd_0882_half_map_1.map.gz emd_0882_half_map_2.map.gz emd_0882_half_map_2.map.gz | 9.6 MB 9.6 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-0882 http://ftp.pdbj.org/pub/emdb/structures/EMD-0882 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0882 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-0882 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6lgpMC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10400 (タイトル: Cryo-EM structure of mouse TRPV3 in a nanodisc EMPIAR-10400 (タイトル: Cryo-EM structure of mouse TRPV3 in a nanodiscData size: 2.1 TB Data #1: Unaligned movies for mouse TRPV3 in a nanodisc [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_0882.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_0882.map.gz / 形式: CCP4 / 大きさ: 15.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.45 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_0882_msk_1.map emd_0882_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_0882_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_0882_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : TRPV3
| 全体 | 名称: TRPV3 |
|---|---|
| 要素 |
|
-超分子 #1: TRPV3
| 超分子 | 名称: TRPV3 / タイプ: organelle_or_cellular_component / ID: 1 / 親要素: 0 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
-分子 #1: Transient receptor potential cation channel subfamily V member 3
| 分子 | 名称: Transient receptor potential cation channel subfamily V member 3 タイプ: protein_or_peptide / ID: 1 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
| 分子量 | 理論値: 73.949867 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: RLKKRIFAAV SEGCVEELRE LLQDLQDLCR RRRGLDVPDF LMHKLTASDT GKTCLMKALL NINPNTKEIV RILLAFAEEN DILDRFINA EYTEEAYEGQ TALNIAIERR QGDITAVLIA AGADVNAHAK GVFFNPKYQH EGFYFGETPL ALAACTNQPE I VQLLMENE ...文字列: RLKKRIFAAV SEGCVEELRE LLQDLQDLCR RRRGLDVPDF LMHKLTASDT GKTCLMKALL NINPNTKEIV RILLAFAEEN DILDRFINA EYTEEAYEGQ TALNIAIERR QGDITAVLIA AGADVNAHAK GVFFNPKYQH EGFYFGETPL ALAACTNQPE I VQLLMENE QTDITSQDSR GNNILHALVT VAEDFKTQND FVKRMYDMIL LRSGNWELET MRNNDGLTPL QLAAKMGKAE IL KYILSRE IKEKPLRSLS RKFTDWAYGP VSSSLYDLTN VDTTTDNSVL EIIVYNTNID NRHEMLTLEP LHTLLHTKWK KFA KYMFFL SFCFYFFYNI TLTLVSYYRP REDEDLPHPL ALTHKMSWLQ LLGRMFVLIW ATCISVKEGI AIFLLRPSDL QSIL SDAWF HFVFFVQAVL VILSVFLYLF AYKEYLACLV LAMALGWANM LYYTRGFQSM GMYSVMIQKV ILHDVLKFLF VYILF LLGF GVALASLIEK CSKDKKDCSS YGSFSDAVLE LFKLTIGLGD LNIQQNSTYP ILFLFLLITY VILTFVLLLN MLIALM GET VENVSKESER IWRLQRARTI LEFEKMLPEW LRSRFRMGEL CKVADEDFRL CLRINEVKWT EWKTHVSFLN EDPGPI UniProtKB: Transient receptor potential cation channel subfamily V member 3 |
-分子 #2: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(tri...
| 分子 | 名称: (2S)-3-(hexadecanoyloxy)-2-[(9Z)-octadec-9-enoyloxy]propyl 2-(trimethylammonio)ethyl phosphate タイプ: ligand / ID: 2 / コピー数: 16 / 式: POV |
|---|---|
| 分子量 | 理論値: 760.076 Da |
| Chemical component information | 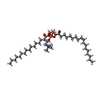 ChemComp-POV: |
-分子 #3: DIUNDECYL PHOSPHATIDYL CHOLINE
| 分子 | 名称: DIUNDECYL PHOSPHATIDYL CHOLINE / タイプ: ligand / ID: 3 / コピー数: 12 / 式: PLC |
|---|---|
| 分子量 | 理論値: 622.834 Da |
| Chemical component information | 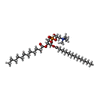 ChemComp-PLC: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.0 mg/mL |
|---|---|
| 緩衝液 | pH: 7.4 |
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER/RHODIUM / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 279 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | #0 - Image recording ID: 1 #0 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #0 - 平均電子線量: 50.0 e/Å2 / #1 - Image recording ID: 2 #1 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #1 - 平均電子線量: 50.0 e/Å2 / #2 - Image recording ID: 3 #2 - フィルム・検出器のモデル: FEI FALCON III (4k x 4k) #2 - 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー














 Z
Z Y
Y X
X



























