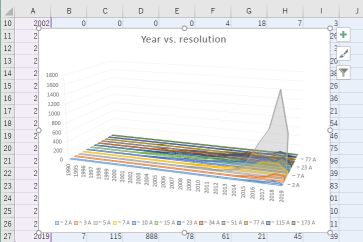
-検索条件
-検索結果
検索 (著者・登録者: shang & g)の結果473件中、1から50件目までを表示しています

EMDB-38156: 
Structure of enterovirus protease in complex host factor
手法: 単粒子 / : Gao X, Cui S

EMDB-36987: 
Structure of CUL3-RBX1-KLHL22 complex without CUL3 NA motif
手法: 単粒子 / : Wang W, Ling L, Dai Z, Zuo P, Yin Y

PDB-8k9i: 
Structure of CUL3-RBX1-KLHL22 complex without CUL3 NA motif
手法: 単粒子 / : Wang W, Ling L, Dai Z, Zuo P, Yin Y

EMDB-39719: 
Focused map of CUL3-RBX1-KLHL22 dimerization region
手法: 単粒子 / : Wang W, Ling L, Dai Z, Zuo P, Yin Y

EMDB-39720: 
Consensus map of CUL3-RBX1-KLHL22 complex
手法: 単粒子 / : Wang W, Ling L, Dai Z, Zuo P, Yin Y

EMDB-39725: 
Cryo-EM structure of CUL3-RBX1-KLHL22 complex --C1 Symmetry
手法: 単粒子 / : Wang W, Ling L, Dai Z, Zuo P, Yin Y

EMDB-35461: 
Protomer 1 and 2 of the asymmetry trimer of the Cul2-Rbx1-EloBC-FEM1B ubiquitin ligase complex
手法: 単粒子 / : Dai Z, Liang L, Yin YX

EMDB-36182: 
An asymmetry dimer of the Cul2-Rbx1-EloBC-FEM1B ubiquitin ligase complexed with BEX2
手法: 単粒子 / : Dai Z, Liang L, Yin YX

EMDB-36183: 
Cryo-EM structure of neddylated Cul2-Rbx1-EloBC-FEM1B complexed with FNIP1-FLCN
手法: 単粒子 / : Dai Z, Liang L, Yin YX

PDB-8ij1: 
Protomer 1 and 2 of the asymmetry trimer of the Cul2-Rbx1-EloBC-FEM1B ubiquitin ligase complex
手法: 単粒子 / : Dai Z, Liang L, Yin YX

PDB-8je1: 
An asymmetry dimer of the Cul2-Rbx1-EloBC-FEM1B ubiquitin ligase complexed with BEX2
手法: 単粒子 / : Dai Z, Liang L, Yin YX

PDB-8je2: 
Cryo-EM structure of neddylated Cul2-Rbx1-EloBC-FEM1B complexed with FNIP1-FLCN
手法: 単粒子 / : Dai Z, Liang L, Yin YX

EMDB-38313: 
Structure of yeast replisome associated with FACT and histone hexamer, the region of FACT-Histones optimized local map
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

EMDB-38314: 
Structure of yeast replisome associated with FACT and histone hexamer,Conformation-2
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

EMDB-38315: 
Structure of yeast replisome associated with FACT and histone hexamer, the region of polymerase epsilon optimized local map
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

EMDB-38316: 
Structure of yeast replisome associated with FACT and histone hexamer, Conformation-1
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

EMDB-38317: 
Structure of yeast replisome associated with FACT and histone hexamer, Composite map
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

PDB-8xgc: 
Structure of yeast replisome associated with FACT and histone hexamer, Composite map
手法: 単粒子 / : Li N, Gao Y, Yu D, Gao N, Zhai Y

EMDB-37006: 
Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with golden hamster ACE2 (local refinement)
手法: 単粒子 / : Niu S, Zhao ZN, Chai Y, Gao GF

EMDB-37090: 
Cryo-EM structure of SARS-CoV-2 BA.3 RBD in complex with golden hamster ACE2 (local refinement)
手法: 単粒子 / : Niu S, Zhao ZN, Chai Y, Gao GF

PDB-8ka8: 
Cryo-EM structure of SARS-CoV-2 Delta RBD in complex with golden hamster ACE2 (local refinement)
手法: 単粒子 / : Niu S, Zhao ZN, Chai Y, Gao GF

PDB-8kc2: 
Cryo-EM structure of SARS-CoV-2 BA.3 RBD in complex with golden hamster ACE2 (local refinement)
手法: 単粒子 / : Niu S, Zhao ZN, Chai Y, Gao GF

EMDB-37852: 
cryo-EM structure of human TMEM63A
手法: 単粒子 / : Yang D

EMDB-36313: 
Cryo-EM structure of apoferritin with MSBP
手法: 単粒子 / : Xu Y, Qin Y, Wang L, Zhang Y, Wang Y, Dang S

EMDB-36314: 
Cryo-EM structure of hemagglutinin with MSBP
手法: 単粒子 / : Xu Y, Qin Y, Wang L, Zhang Y, Wang Y, Dang S
EMDB-36315: 
Cryo-EM structure of catalase with MSBP
手法: 単粒子 / : Xu Y, Qin Y, Wang L, Zhang Y, Wang Y, Dang S

EMDB-36316: 
Cryo-EM structure of beta-Galactosidase with MSBP
手法: 単粒子 / : Xu Y, Qin Y, Wang L, Zhang Y, Wang Y, Dang S
EMDB-37356: 
Cryo-EM structure of the GPR101-Gs complex
手法: 単粒子 / : Sun JP, Gao N, Yu X, Wang GP, Yang F, Wang JY, Yang Z, Guan Y

EMDB-37357: 
Cryo-EM structure of the AA-14-bound GPR101-Gs complex
手法: 単粒子 / : Sun JP, Yu X, Gao N, Yang F, Wang JY, Yang Z, Guan Y, Wang GP

EMDB-37358: 
Cryo-EM structure of the AA14-bound GPR101 complex
手法: 単粒子 / : Sun JP, Yu X, Gao N, Yang F, Wang JY, Yang Z, Guan Y, Wang GP

PDB-8w8q: 
Cryo-EM structure of the GPR101-Gs complex
手法: 単粒子 / : Sun JP, Gao N, Yu X, Wang GP, Yang F, Wang JY, Yang Z, Guan Y

PDB-8w8r: 
Cryo-EM structure of the AA-14-bound GPR101-Gs complex
手法: 単粒子 / : Sun JP, Yu X, Gao N, Yang F, Wang JY, Yang Z, Guan Y, Wang GP

PDB-8w8s: 
Cryo-EM structure of the AA14-bound GPR101 complex
手法: 単粒子 / : Sun JP, Yu X, Gao N, Yang F, Wang JY, Yang Z, Guan Y, Wang GP

EMDB-37429: 
Cryo-EM structure of the SEP363856-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37430: 
Cryo-EM structure of the ZH8651-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37431: 
Cryo-EM structure of the TMA-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37432: 
Cryo-EM structure of the PEA-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37433: 
Cryo-EM structure of the ZH8667-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37434: 
Cryo-EM structure of the ZH8651-bound hTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37435: 
Cryo-EM structure of the ZH8651-bound mTAAR1-Gq complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37436: 
Cryo-EM structure of the PEA-bound hTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37437: 
Cryo-EM structure of the CHA-bound mTAAR1-Gq complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

EMDB-37438: 
Cryo-EM structure of the CHA-bound mTAAR1 complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

PDB-8wc3: 
Cryo-EM structure of the SEP363856-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

PDB-8wc4: 
Cryo-EM structure of the ZH8651-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP

PDB-8wc5: 
Cryo-EM structure of the TMA-bound mTAAR1-Gs complex
手法: 単粒子 / : Rong NK, Guo LL, Zhang MH, Li Q, Yang F, Sun JP
ページ:
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア EMN検索について
EMN検索について







 wwPDBはEMDBデータモデルのバージョン3へ移行します
wwPDBはEMDBデータモデルのバージョン3へ移行します