+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of BTV empty pre-core | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード |  Bluetongue virus (ブルータング) / Bluetongue virus (ブルータング) /  capsid protein (カプシド) / assembly intermediate / pre-core / capsid protein (カプシド) / assembly intermediate / pre-core /  VIRUS (ウイルス) VIRUS (ウイルス) | |||||||||
| 生物種 |   Bluetongue virus (serotype 1 / isolate South Africa) (ブルータング) Bluetongue virus (serotype 1 / isolate South Africa) (ブルータング) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.2 Å クライオ電子顕微鏡法 / 解像度: 3.2 Å | |||||||||
 データ登録者 データ登録者 | Xia X / Sung PY / Martynowycz MW / Gonen T / Roy P / Zhou ZH | |||||||||
| 資金援助 |  米国, 米国,  英国, 2件 英国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Cell / 年: 2024 ジャーナル: Cell / 年: 2024タイトル: RNA genome packaging and capsid assembly of bluetongue virus visualized in host cells. 著者: Xian Xia / Po-Yu Sung / Michael W Martynowycz / Tamir Gonen / Polly Roy / Z Hong Zhou /   要旨: Unlike those of double-stranded DNA (dsDNA), single-stranded DNA (ssDNA), and ssRNA viruses, the mechanism of genome packaging of dsRNA viruses is poorly understood. Here, we combined the techniques ...Unlike those of double-stranded DNA (dsDNA), single-stranded DNA (ssDNA), and ssRNA viruses, the mechanism of genome packaging of dsRNA viruses is poorly understood. Here, we combined the techniques of high-resolution cryoelectron microscopy (cryo-EM), cellular cryoelectron tomography (cryo-ET), and structure-guided mutagenesis to investigate genome packaging and capsid assembly of bluetongue virus (BTV), a member of the Reoviridae family of dsRNA viruses. A total of eleven assembly states of BTV capsid were captured, with resolutions up to 2.8 Å, with most visualized in the host cytoplasm. ATPase VP6 was found underneath the vertices of capsid shell protein VP3 as an RNA-harboring pentamer, facilitating RNA packaging. RNA packaging expands the VP3 shell, which then engages middle- and outer-layer proteins to generate infectious virions. These revealed "duality" characteristics of the BTV assembly mechanism reconcile previous contradictory co-assembly and core-filling models and provide insights into the mysterious RNA packaging and capsid assembly of Reoviridae members and beyond. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_43725.map.gz emd_43725.map.gz | 192.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-43725-v30.xml emd-43725-v30.xml emd-43725.xml emd-43725.xml | 15.6 KB 15.6 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_43725.png emd_43725.png | 80.1 KB | ||
| Filedesc metadata |  emd-43725.cif.gz emd-43725.cif.gz | 4.5 KB | ||
| その他 |  emd_43725_half_map_1.map.gz emd_43725_half_map_1.map.gz emd_43725_half_map_2.map.gz emd_43725_half_map_2.map.gz | 170.3 MB 170.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-43725 http://ftp.pdbj.org/pub/emdb/structures/EMD-43725 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43725 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-43725 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_43725.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_43725.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_43725_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
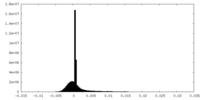
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_43725_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
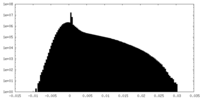
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Bluetongue virus (serotype 1 / isolate South Africa)
| 全体 | 名称:   Bluetongue virus (serotype 1 / isolate South Africa) (ブルータング) Bluetongue virus (serotype 1 / isolate South Africa) (ブルータング) |
|---|---|
| 要素 |
|
-超分子 #1: Bluetongue virus (serotype 1 / isolate South Africa)
| 超分子 | 名称: Bluetongue virus (serotype 1 / isolate South Africa) タイプ: virus / ID: 1 / 親要素: 0 / NCBI-ID: 10905 生物種: Bluetongue virus (serotype 1 / isolate South Africa) ウイルスタイプ: VIRION / ウイルス・単離状態: SPECIES / ウイルス・エンベロープ: No / ウイルス・中空状態: No |
|---|---|
| 宿主 | 生物種:   Ovis aries (ヒツジ) Ovis aries (ヒツジ) |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8.8 / 構成要素 - 濃度: 20.0 mM 構成要素 - 名称: Tris  トリスヒドロキシメチルアミノメタン トリスヒドロキシメチルアミノメタン |
|---|---|
| グリッド | モデル: PELCO Ultrathin Carbon with Lacey Carbon / 材質: COPPER / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: CONTINUOUS / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 281.15 K / 装置: FEI VITROBOT MARK IV |
| 詳細 | Virus isolated from infected BHK cells |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 1.8 µm / 倍率(公称値): 81000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 1.8 µm / 倍率(公称値): 81000 |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Bioquantum / エネルギーフィルター - スリット幅: 20 eV |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 3 / 実像数: 62928 / 平均露光時間: 2.0 sec. / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 粒子像選択 | 選択した数: 130380 |
|---|---|
| 初期モデル | モデルのタイプ: OTHER |
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 3次元分類 | クラス数: 3 / 平均メンバー数/クラス: 50000 / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD / ソフトウェア - 名称: RELION (ver. 3.1) |
| 最終 再構成 | 使用したクラス数: 1 / 想定した対称性 - 点群: C5 (5回回転対称 ) / 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 79473 ) / 解像度のタイプ: BY AUTHOR / 解像度: 3.2 Å / 解像度の算出法: FSC 0.143 CUT-OFF / ソフトウェア - 名称: RELION (ver. 3.1) / 使用した粒子像数: 79473 |
 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)