+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | E. coli SIR2-HerA complex (dodecamer SIR2 bound 4 protomers of HerA) | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HerA /  SIR2 / NADase / SIR2 / NADase /  ATPase (ATPアーゼ) / Anti-phage / ATPase (ATPアーゼ) / Anti-phage /  IMMUNE SYSTEM (免疫系) IMMUNE SYSTEM (免疫系) | |||||||||
| 機能・相同性 | Helicase HerA, central domain / Helicase HerA, central domain / SIR2-like domain / SIR2-like domain /  hydrolase activity / P-loop containing nucleoside triphosphate hydrolase / SIR2-like domain-containing protein / Nucleoside triphosphate hydrolase hydrolase activity / P-loop containing nucleoside triphosphate hydrolase / SIR2-like domain-containing protein / Nucleoside triphosphate hydrolase 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) | |||||||||
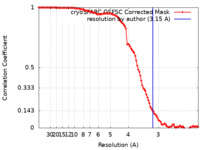
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.15 Å クライオ電子顕微鏡法 / 解像度: 3.15 Å | |||||||||
 データ登録者 データ登録者 | Shen ZF / Lin QP / Fu TM | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2023 ジャーナル: Mol Cell / 年: 2023タイトル: Assembly-mediated activation of the SIR2-HerA supramolecular complex for anti-phage defense. 著者: Zhangfei Shen / Qingpeng Lin / Xiao-Yuan Yang / Elizabeth Fosuah / Tian-Min Fu /  要旨: SIR2-HerA, a bacterial two-protein anti-phage defense system, induces bacterial death by depleting NAD upon phage infection. Biochemical reconstitution of SIR2, HerA, and the SIR2-HerA complex ...SIR2-HerA, a bacterial two-protein anti-phage defense system, induces bacterial death by depleting NAD upon phage infection. Biochemical reconstitution of SIR2, HerA, and the SIR2-HerA complex reveals a dynamic assembly process. Unlike other ATPases, HerA can form various oligomers, ranging from dimers to nonamers. When assembled with SIR2, HerA forms a hexamer and converts SIR2 from a nuclease to an NAD hydrolase, representing an unexpected regulatory mechanism mediated by protein assembly. Furthermore, high concentrations of ATP can inhibit NAD hydrolysis by the SIR2-HerA complex. Cryo-EM structures of the SIR2-HerA complex reveal a giant supramolecular assembly up to 1 MDa, with SIR2 as a dodecamer and HerA as a hexamer, crucial for anti-phage defense. Unexpectedly, the HerA hexamer resembles a spiral staircase and exhibits helicase activities toward dual-forked DNA. Together, we reveal the supramolecular assembly of SIR2-HerA as a unique mechanism for switching enzymatic activities and bolstering anti-phage defense strategies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_40778.map.gz emd_40778.map.gz | 118.1 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-40778-v30.xml emd-40778-v30.xml emd-40778.xml emd-40778.xml | 18.7 KB 18.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_40778_fsc.xml emd_40778_fsc.xml | 10.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_40778.png emd_40778.png | 106.3 KB | ||
| Filedesc metadata |  emd-40778.cif.gz emd-40778.cif.gz | 6.1 KB | ||
| その他 |  emd_40778_additional_1.map.gz emd_40778_additional_1.map.gz emd_40778_half_map_1.map.gz emd_40778_half_map_1.map.gz emd_40778_half_map_2.map.gz emd_40778_half_map_2.map.gz | 108.7 MB 116.1 MB 116.1 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-40778 http://ftp.pdbj.org/pub/emdb/structures/EMD-40778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40778 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-40778 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_40778.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_40778.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.11 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-追加マップ: #1
| ファイル | emd_40778_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
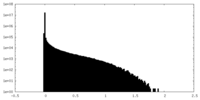
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_40778_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
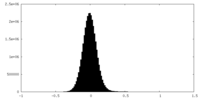
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_40778_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
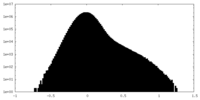
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : SIR2-HerA complex(dodecomaer SIR2 bound with four protomers of HerA)
| 全体 | 名称: SIR2-HerA complex(dodecomaer SIR2 bound with four protomers of HerA) |
|---|---|
| 要素 |
|
-超分子 #1: SIR2-HerA complex(dodecomaer SIR2 bound with four protomers of HerA)
| 超分子 | 名称: SIR2-HerA complex(dodecomaer SIR2 bound with four protomers of HerA) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 / 詳細: dodecomaer SIR2 bound with four protomers of HerA |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
-分子 #1: SIR2-like domain-containing protein
| 分子 | 名称: SIR2-like domain-containing protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 12 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 46.817664 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSIYQGGNKL NEDDFRSHVY SLCQLDNVGV LLGAGASVGC GGKTMKDVWK SFKQNYPELL GALIDKYLLV SQIDSDNNLV NVELLIDEA TKFLSVAKTR RCEDEEEEFR KILSSLYKEV TKAALLTGEQ FREKNQGKKD AFKYHKELIS KLISNRQPGQ S APAIFTTN ...文字列: MSIYQGGNKL NEDDFRSHVY SLCQLDNVGV LLGAGASVGC GGKTMKDVWK SFKQNYPELL GALIDKYLLV SQIDSDNNLV NVELLIDEA TKFLSVAKTR RCEDEEEEFR KILSSLYKEV TKAALLTGEQ FREKNQGKKD AFKYHKELIS KLISNRQPGQ S APAIFTTN YDLALEWAAE DLGIQLFNGF SGLHTRQFYP QNFDLAFRNV NAKGEARFGH YHAYLYKLHG SLTWYQNDSL TV NEVSASQ AYDEYINDII NKDDFYRGQH LIYPGANKYS HTIGFVYGEM FRRFGEFISK PQTALFINGF GFGDYHINRI ILG ALLNPS FHVVIYYPEL KEAITKVSKG GGSEAEKAIV TLKNMAFNQV TVVGGGSKAY FNSFVEHLPY PVLFPRDNIV DELV EAIAN LSKGEGNVPF UniProtKB: SIR2-like domain-containing protein |
-分子 #2: Nucleoside triphosphate hydrolase
| 分子 | 名称: Nucleoside triphosphate hydrolase / タイプ: protein_or_peptide / ID: 2 / コピー数: 4 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 分子量 | 理論値: 68.431992 KDa |
| 組換発現 | 生物種:   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
| 配列 | 文字列: MSLFKLTEIS AIGYVVGLEG ERIRINLHEG LQGRLASHRK GVSSVTQPGD LIGFDAGNIL VVARVTDMAF VEADKAHKAN VGTSDLADI PLRQIIAYAI GFVKRELNGY VFISEDWRLP ALGSSAVPLT SDFLNIIYSI DKEELPKAVE LGVDSRTKTV K IFASVDKL ...文字列: MSLFKLTEIS AIGYVVGLEG ERIRINLHEG LQGRLASHRK GVSSVTQPGD LIGFDAGNIL VVARVTDMAF VEADKAHKAN VGTSDLADI PLRQIIAYAI GFVKRELNGY VFISEDWRLP ALGSSAVPLT SDFLNIIYSI DKEELPKAVE LGVDSRTKTV K IFASVDKL LSRHLAVLGS TGYGKSNFNA LLTRKVSEKY PNSRIVIFDI NGEYAQAFTG IPNVKHTILG ESPNVDSLEK KQ QKGELYS EEYYCYKKIP YQALGFAGLI KLLRPSDKTQ LPALRNALSA INRTHFKSRN IYLEKDDGET FLLYDDCRDT NQS KLAEWL DLLRRRRLKR TNVWPPFKSL ATLVAEFGCV AADRSNGSKR DAFGFSNVLP LVKIIQQLAE DIRFKSIVNL NGGG ELADG GTHWDKAMSD EVDYFFGKEK GQENDWNVHI VNMKNLAQDH APMLLSALLE MFAEILFRRG QERSYPTVLL LEEAH HYLR DPYAEIDSQI KAYERLAKEG RKFKCSLIVS TQRPSELSPT VLAMCSNWFS LRLTNERDLQ ALRYAMESGN EQILKQ ISG LPRGDAVAFG SAFNLPVRIS INQARPGPKS SDAVFSEEWA NCTELRC UniProtKB: Nucleoside triphosphate hydrolase |
-分子 #3: [(2R,3S,4R,5R)-5-(6-AMINOPURIN-9-YL)-3,4-DIHYDROXY-OXOLAN-2-YL]ME...
| 分子 | 名称: [(2R,3S,4R,5R)-5-(6-AMINOPURIN-9-YL)-3,4-DIHYDROXY-OXOLAN-2-YL]METHYL [HYDROXY-[[(2R,3S,4R,5S)-3,4,5-TRIHYDROXYOXOLAN-2-YL]METHOXY]PHOSPHORYL] HYDROGEN PHOSPHATE タイプ: ligand / ID: 3 / コピー数: 12 / 式: AR6 |
|---|---|
| 分子量 | 理論値: 559.316 Da |
-分子 #4: ADENOSINE-5'-DIPHOSPHATE
| 分子 | 名称: ADENOSINE-5'-DIPHOSPHATE / タイプ: ligand / ID: 4 / コピー数: 3 / 式: ADP |
|---|---|
| 分子量 | 理論値: 427.201 Da |
| Chemical component information | 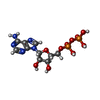 ChemComp-ADP: |
-分子 #5: MAGNESIUM ION
| 分子 | 名称: MAGNESIUM ION / タイプ: ligand / ID: 5 / コピー数: 3 / 式: MG |
|---|---|
| 分子量 | 理論値: 24.305 Da |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.5 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 平均電子線量: 50.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー

















 Z
Z Y
Y X
X