+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6eno | ||||||
|---|---|---|---|---|---|---|---|
| Title | Double cubane cluster oxidoreductase | ||||||
 Components Components | Dehydratase family protein | ||||||
 Keywords Keywords |  OXIDOREDUCTASE / double cubane cluster / OXIDOREDUCTASE / double cubane cluster /  iron-sulfur protein / acetylene reduction iron-sulfur protein / acetylene reduction | ||||||
| Function / homology | : / FldB/FldC dehydratase alpha/beta subunit / 2-hydroxyglutaryl-CoA dehydratase, D-component /  hydro-lyase activity / Double cubane cluster / hydro-lyase activity / Double cubane cluster /  CITRIC ACID / Dehydratase family protein CITRIC ACID / Dehydratase family protein Function and homology information Function and homology information | ||||||
| Biological species |    Carboxydothermus hydrogenoformans (bacteria) Carboxydothermus hydrogenoformans (bacteria) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 1.635 Å SAD / Resolution: 1.635 Å | ||||||
 Authors Authors | Jeoung, J.H. / Dobbek, H. | ||||||
| Funding support |  Germany, 1items Germany, 1items
| ||||||
 Citation Citation |  Journal: Proc. Natl. Acad. Sci. U.S.A. / Year: 2018 Journal: Proc. Natl. Acad. Sci. U.S.A. / Year: 2018Title: ATP-dependent substrate reduction at an [Fe8S9] double-cubane cluster. Authors: Jeoung, J.H. / Dobbek, H. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6eno.cif.gz 6eno.cif.gz | 270.4 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6eno.ent.gz pdb6eno.ent.gz | 221.7 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6eno.json.gz 6eno.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/en/6eno https://data.pdbj.org/pub/pdb/validation_reports/en/6eno ftp://data.pdbj.org/pub/pdb/validation_reports/en/6eno ftp://data.pdbj.org/pub/pdb/validation_reports/en/6eno | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||||||||
| Unit cell |
| |||||||||||||||
| Components on special symmetry positions |
|
- Components
Components
| #1: Protein | Mass: 47762.891 Da / Num. of mol.: 1 Source method: isolated from a genetically manipulated source Details: N-TERMINAL Gly-Ala residues are from cloning artifact. Source: (gene. exp.)    Carboxydothermus hydrogenoformans (strain ATCC BAA-161 / DSM 6008 / Z-2901) (bacteria) Carboxydothermus hydrogenoformans (strain ATCC BAA-161 / DSM 6008 / Z-2901) (bacteria)Gene: CHY_0487 / Production host:   Escherichia coli (E. coli) / References: UniProt: Q3AET9 Escherichia coli (E. coli) / References: UniProt: Q3AET9 | ||
|---|---|---|---|
| #2: Chemical | ChemComp-BJ8 / | ||
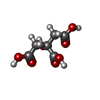
| #3: Chemical | ChemComp-CIT /  Citric acid Citric acid | ||
| #4: Chemical |  Glycerol Glycerol#5: Water | ChemComp-HOH / |  Water Water |
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.13 Å3/Da / Density % sol: 42.22 % |
|---|---|
Crystal grow | Temperature: 291.15 K / Method: vapor diffusion, hanging drop / Details: PEG 8000, Na-citrate, Na-dithinite |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  BESSY BESSY  / Beamline: 14.1 / Wavelength: 0.9184 Å / Beamline: 14.1 / Wavelength: 0.9184 Å |
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Jun 27, 2016 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength : 0.9184 Å / Relative weight: 1 : 0.9184 Å / Relative weight: 1 |
| Reflection | Resolution: 1.63→42.9 Å / Num. obs: 51968 / % possible obs: 98.8 % / Redundancy: 7 % / Net I/σ(I): 13.9 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure : :  SAD / Resolution: 1.635→34.456 Å / SU ML: 0.2 / Cross valid method: FREE R-VALUE / σ(F): 2 / Phase error: 21.21 SAD / Resolution: 1.635→34.456 Å / SU ML: 0.2 / Cross valid method: FREE R-VALUE / σ(F): 2 / Phase error: 21.21
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.635→34.456 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller













 PDBj
PDBj