+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | STRUCTURE OF PHOTOSYNTHETIC LH1-RC SUPER-COMPLEX OF RHODOBACTER SPHAEROIDES LACKING PROTEIN-U | |||||||||||||||||||||
 マップデータ マップデータ | ||||||||||||||||||||||
 試料 試料 |
| |||||||||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報organelle inner membrane / plasma membrane-derived chromatophore membrane / plasma membrane light-harvesting complex /  bacteriochlorophyll binding / photosynthetic electron transport in photosystem II / bacteriochlorophyll binding / photosynthetic electron transport in photosystem II /  photosynthesis, light reaction / electron transporter, transferring electrons within the cyclic electron transport pathway of photosynthesis activity / membrane => GO:0016020 / photosynthesis, light reaction / electron transporter, transferring electrons within the cyclic electron transport pathway of photosynthesis activity / membrane => GO:0016020 /  metal ion binding / metal ion binding /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||||||||||||||
| 生物種 |  Rhodobacter sphaeroides f. sp. denitrificans (バクテリア) Rhodobacter sphaeroides f. sp. denitrificans (バクテリア) | |||||||||||||||||||||
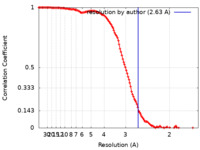
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 2.63 Å クライオ電子顕微鏡法 / 解像度: 2.63 Å | |||||||||||||||||||||
 データ登録者 データ登録者 | Tani K / Kanno R / Kawamura S / Kikuchi R / Nagashima KVP / Hall M / Takahashi A / Yu L-J / Kimura Y / Madigan MT ...Tani K / Kanno R / Kawamura S / Kikuchi R / Nagashima KVP / Hall M / Takahashi A / Yu L-J / Kimura Y / Madigan MT / Mizoguchi A / Humbel BM / Wang-Otomo Z-Y | |||||||||||||||||||||
| 資金援助 |  日本, 6件 日本, 6件
| |||||||||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2022 ジャーナル: Nat Commun / 年: 2022タイトル: Asymmetric structure of the native Rhodobacter sphaeroides dimeric LH1-RC complex. 著者: Kazutoshi Tani / Ryo Kanno / Riku Kikuchi / Saki Kawamura / Kenji V P Nagashima / Malgorzata Hall / Ai Takahashi / Long-Jiang Yu / Yukihiro Kimura / Michael T Madigan / Akira Mizoguchi / ...著者: Kazutoshi Tani / Ryo Kanno / Riku Kikuchi / Saki Kawamura / Kenji V P Nagashima / Malgorzata Hall / Ai Takahashi / Long-Jiang Yu / Yukihiro Kimura / Michael T Madigan / Akira Mizoguchi / Bruno M Humbel / Zheng-Yu Wang-Otomo /    要旨: Rhodobacter sphaeroides is a model organism in bacterial photosynthesis, and its light-harvesting-reaction center (LH1-RC) complex contains both dimeric and monomeric forms. Here we present cryo-EM ...Rhodobacter sphaeroides is a model organism in bacterial photosynthesis, and its light-harvesting-reaction center (LH1-RC) complex contains both dimeric and monomeric forms. Here we present cryo-EM structures of the native LH1-RC dimer and an LH1-RC monomer lacking protein-U (ΔU). The native dimer reveals several asymmetric features including the arrangement of its two monomeric components, the structural integrity of protein-U, the overall organization of LH1, and rigidities of the proteins and pigments. PufX plays a critical role in connecting the two monomers in a dimer, with one PufX interacting at its N-terminus with another PufX and an LH1 β-polypeptide in the other monomer. One protein-U was only partially resolved in the dimeric structure, signaling different degrees of disorder in the two monomers. The ΔU LH1-RC monomer was half-moon-shaped and contained 11 α- and 10 β-polypeptides, indicating a critical role for protein-U in controlling the number of αβ-subunits required for dimer assembly and stabilization. These features are discussed in relation to membrane topology and an assembly model proposed for the native dimeric complex. | |||||||||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_32193.map.gz emd_32193.map.gz | 167 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-32193-v30.xml emd-32193-v30.xml emd-32193.xml emd-32193.xml | 23.1 KB 23.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_32193_fsc.xml emd_32193_fsc.xml | 12.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_32193.png emd_32193.png | 135.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-32193 http://ftp.pdbj.org/pub/emdb/structures/EMD-32193 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32193 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-32193 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7vy3MC  7vy2C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_32193.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_32193.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Photosynthetic LH1-RC complex from the purple phototrophic bacter...
+超分子 #1: Photosynthetic LH1-RC complex from the purple phototrophic bacter...
+超分子 #2: Rhodobacter sphaeroides monomeric LH1-RC Complex lacking protein-U
+分子 #1: Photosynthetic reaction center L subunit
+分子 #2: Reaction center protein M chain
+分子 #3: Photosynthetic reaction center subunit H
+分子 #4: Antenna pigment protein alpha chain
+分子 #5: Antenna pigment protein beta chain
+分子 #6: PufX
+分子 #7: BACTERIOCHLOROPHYLL A
+分子 #8: BACTERIOPHEOPHYTIN A
+分子 #9: UBIQUINONE-10
+分子 #10: (1R)-2-{[{[(2S)-2,3-DIHYDROXYPROPYL]OXY}(HYDROXY)PHOSPHORYL]OXY}-...
+分子 #11: LAURYL DIMETHYLAMINE-N-OXIDE
+分子 #12: DODECYL-BETA-D-MALTOSIDE
+分子 #13: FE (III) ION
+分子 #14: SPHEROIDENE
+分子 #15: CARDIOLIPIN
+分子 #16: PHOSPHATIDYLETHANOLAMINE
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 3.0 mg/mL |
|---|---|
| 緩衝液 | pH: 8 |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 80 % / チャンバー内温度: 277 K / 装置: LEICA EM GP |
| 詳細 | This sample was monodisperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: COUNTING / 平均露光時間: 1.275 sec. / 平均電子線量: 42.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
 ムービー
ムービー コントローラー
コントローラー