+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of hMPV preF bound by Fabs MPE8 and SAN32-2 | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 | Precursor fusion glycoprotein F0, Paramyxoviridae / Fusion glycoprotein F0 / fusion of virus membrane with host plasma membrane / host cell plasma membrane / virion membrane /  細胞膜 / Fusion glycoprotein F0 細胞膜 / Fusion glycoprotein F0 機能・相同性情報 機能・相同性情報 | |||||||||
| 生物種 |   Human metapneumovirus (ヒトメタニューモウイルス) / Human metapneumovirus (ヒトメタニューモウイルス) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.06 Å クライオ電子顕微鏡法 / 解像度: 3.06 Å | |||||||||
 データ登録者 データ登録者 | Rush SA / Hsieh C-L / McLellan JS | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Cell Rep / 年: 2022 ジャーナル: Cell Rep / 年: 2022タイトル: Characterization of prefusion-F-specific antibodies elicited by natural infection with human metapneumovirus. 著者: Scott A Rush / Gurpreet Brar / Ching-Lin Hsieh / Emilie Chautard / Jennifer N Rainho-Tomko / Chris D Slade / Christine A Bricault / Ana Kume / James Kearns / Rachel Groppo / Sophia T Mundle / ...著者: Scott A Rush / Gurpreet Brar / Ching-Lin Hsieh / Emilie Chautard / Jennifer N Rainho-Tomko / Chris D Slade / Christine A Bricault / Ana Kume / James Kearns / Rachel Groppo / Sophia T Mundle / Linong Zhang / Danilo Casimiro / Tong-Ming Fu / Joshua M DiNapoli / Jason S McLellan /   要旨: Human metapneumovirus (hMPV) is a major cause of acute respiratory infections in infants and older adults, for which no vaccines or therapeutics are available. The viral fusion (F) glycoprotein is ...Human metapneumovirus (hMPV) is a major cause of acute respiratory infections in infants and older adults, for which no vaccines or therapeutics are available. The viral fusion (F) glycoprotein is required for entry and is the primary target of neutralizing antibodies; however, little is known about the humoral immune response generated from natural infection. Here, using prefusion-stabilized F proteins to interrogate memory B cells from two older adults, we obtain over 700 paired non-IgM antibody sequences representing 563 clonotypes, indicative of a highly polyclonal response. Characterization of 136 monoclonal antibodies reveals broad recognition of the protein surface, with potently neutralizing antibodies targeting each antigenic site. Cryo-EM studies further reveal two non-canonical sites and the molecular basis for recognition of the apex of hMPV F by two prefusion-specific neutralizing antibodies. Collectively, these results provide insight into the humoral response to hMPV infection in older adults and will help guide vaccine development. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_25982.map.gz emd_25982.map.gz | 30.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-25982-v30.xml emd-25982-v30.xml emd-25982.xml emd-25982.xml | 17.9 KB 17.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_25982.png emd_25982.png | 109.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-25982 http://ftp.pdbj.org/pub/emdb/structures/EMD-25982 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25982 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-25982 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7tl0MC  7tjqC C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_25982.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_25982.map.gz / 形式: CCP4 / 大きさ: 64 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.36688 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Trimeric prefusion hMPV F glycoprotein bound by three molecules o...
| 全体 | 名称: Trimeric prefusion hMPV F glycoprotein bound by three molecules of Fabs SAN32-2 and MPE8 |
|---|---|
| 要素 |
|
-超分子 #1: Trimeric prefusion hMPV F glycoprotein bound by three molecules o...
| 超分子 | 名称: Trimeric prefusion hMPV F glycoprotein bound by three molecules of Fabs SAN32-2 and MPE8 タイプ: complex / キメラ: Yes / ID: 1 / 親要素: 0 / 含まれる分子: #1-#5 |
|---|---|
| 由来(天然) | 生物種:   Human metapneumovirus (ヒトメタニューモウイルス) Human metapneumovirus (ヒトメタニューモウイルス) |
| 分子量 | 理論値: 457.9 kDa/nm |
-分子 #1: Fusion glycoprotein F0
| 分子 | 名称: Fusion glycoprotein F0 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Human metapneumovirus (ヒトメタニューモウイルス) Human metapneumovirus (ヒトメタニューモウイルス) |
| 分子量 | 理論値: 60.453852 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: MSWKVVIIFS LLITPQHGLK ESYLEESCST ITEGYLSVLR TGWYTNVFTL EVGDVENLTC ADGPSLIKTE LDLTKSALRE LRTVSADQL AREEQIENPR RRRFVLGAIA CGVATAAAVT AGVAIAKCIR LESEVTAIKN CLKKTNECVS TLGCGVRVLA T AVRELKDF ...文字列: MSWKVVIIFS LLITPQHGLK ESYLEESCST ITEGYLSVLR TGWYTNVFTL EVGDVENLTC ADGPSLIKTE LDLTKSALRE LRTVSADQL AREEQIENPR RRRFVLGAIA CGVATAAAVT AGVAIAKCIR LESEVTAIKN CLKKTNECVS TLGCGVRVLA T AVRELKDF VSKNLTRAIN KNKCDIPDLK MAVSFSQFNR RFLNVVRQFS DNAGITPAIS KDLMTDAELA RAISNMPTSA GQ IKLMLEN RAMVRRKGFG ILIGVYGSSV IYMVQLPIFG VIDTPCWIVK AAPSCSEKKG NYACLLREDQ GWYCQNAGST VYY PCEKDC ETRGDHVFCD TAAGINVAEQ SKECNINIST TNYPCKVSCG RHPISMVALS PLGALVACYK GVSCSIGSNR VGII KQLNK GCSYITNQDA DTVTIDNTVY QLSKVEGEQH VIKGRPVSSS FDPVKFPQDQ FNVALDQCFE SIENSQALVD QSNRI LSSA EKGNTGGGGS GYIPEAPRDG QAYVRKDGEW VLLSTFLGRS LEVLFQGPGH HHHHHHHSAW SHPQFEK |
-分子 #2: SAN32-2 Fab heavy chain
| 分子 | 名称: SAN32-2 Fab heavy chain / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 24.099031 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVQSGAE VKKPGESLRI SCKSSGYTFT TYWITWVRQM PGKGLEWMGR IDPSDSYTDY SPSFKGHVTI SVDKSINTAY LQWGSLKSS DTAIFYCARQ ASSGKIYFDY WGQGTLVTVS SASTKGPSVF PLAPSSKSTS GGTAALGCLV KDYFPEPVTV S WNSGALTS ...文字列: EVQLVQSGAE VKKPGESLRI SCKSSGYTFT TYWITWVRQM PGKGLEWMGR IDPSDSYTDY SPSFKGHVTI SVDKSINTAY LQWGSLKSS DTAIFYCARQ ASSGKIYFDY WGQGTLVTVS SASTKGPSVF PLAPSSKSTS GGTAALGCLV KDYFPEPVTV S WNSGALTS GVHTFPAVLQ SSGLYSLSSV VTVPSSSLGT QTYICNVNHK PSNTKVDKKV EPKSCD |
-分子 #3: SAN32-2 Fab light chain
| 分子 | 名称: SAN32-2 Fab light chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.542988 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: DIQMTQSPSS LSASVGDRVT ITCQASQGIN YYLNWYQQKP GKAPKVLIYD ASDLETGVPS RFSGGGSGTH FTFTISSLQT EDIGTYYCQ QYDNLPFTFG QGTRLEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS ...文字列: DIQMTQSPSS LSASVGDRVT ITCQASQGIN YYLNWYQQKP GKAPKVLIYD ASDLETGVPS RFSGGGSGTH FTFTISSLQT EDIGTYYCQ QYDNLPFTFG QGTRLEIKRT VAAPSVFIFP PSDEQLKSGT ASVVCLLNNF YPREAKVQWK VDNALQSGNS Q ESVTEQDS KDSTYSLSST LTLSKADYEK HKVYACEVTH QGLSSPVTKS FNRGEC |
-分子 #4: MPE8 Fab heavy chain
| 分子 | 名称: MPE8 Fab heavy chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 23.985793 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: EVQLVESGGG LVKPGGSLRL SCAASGFTFS SYSMNWVRQA PGKGLEWVSS ISASSSYSDY ADSAKGRFTI SRDNAKTSLF LQMNSLRAE DTAIYFCARA RATGYSSITP YFDIWGQGTL VTVSSASTKG PSVFPLAPSS KSTSGGTAAL GCLVKDYFPE P VTVSWNSG ...文字列: EVQLVESGGG LVKPGGSLRL SCAASGFTFS SYSMNWVRQA PGKGLEWVSS ISASSSYSDY ADSAKGRFTI SRDNAKTSLF LQMNSLRAE DTAIYFCARA RATGYSSITP YFDIWGQGTL VTVSSASTKG PSVFPLAPSS KSTSGGTAAL GCLVKDYFPE P VTVSWNSG ALTSGVHTFP AVLQSSGLYS LSSVVTVPSS SLGTQTYICN VNHKPSNTKV DKKVEPKSCD |
-分子 #5: MPE8 Fab light chain
| 分子 | 名称: MPE8 Fab light chain / タイプ: protein_or_peptide / ID: 5 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 22.772092 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QSVVTQPPSV SGAPGQRVTI SCTGSSSNIG AGYDVHWYQQ LPGTAPKLLI YDNNNRPSGV PDRFSASKSG TSASLAITGL QAEDEADYY CQSYDRSLSG VFGTGTKVTV LGQPKAAPSV TLFPPSSEEL QANKATLVCL ISDFYPGAVT VAWKADSSPV K AGVETTTP ...文字列: QSVVTQPPSV SGAPGQRVTI SCTGSSSNIG AGYDVHWYQQ LPGTAPKLLI YDNNNRPSGV PDRFSASKSG TSASLAITGL QAEDEADYY CQSYDRSLSG VFGTGTKVTV LGQPKAAPSV TLFPPSSEEL QANKATLVCL ISDFYPGAVT VAWKADSSPV K AGVETTTP SKQSNNKYAA SSYLSLTPEQ WKSHKSYSCQ VTHEGSTVEK TVAPTECS |
-分子 #7: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 7 / コピー数: 6 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information | 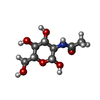 ChemComp-NAG: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 構成要素:
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| グリッド | モデル: C-flat-1.2/1.3 / 材質: COPPER / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: PLASMA CLEANING / 前処理 - 雰囲気: OTHER | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 283.15 K / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 29000 Bright-field microscopy / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.2 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 29000 |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 1 / 実像数: 3636 / 平均電子線量: 70.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 粒子像選択 | 選択した数: 772860 |
|---|---|
| CTF補正 | ソフトウェア - 名称: cryoSPARC (ver. 3.2.0) / ソフトウェア - 詳細: cryoSPARC Live |
| 初期モデル | モデルのタイプ: NONE / 詳細: ab-initio |
| 初期 角度割当 | タイプ: RANDOM ASSIGNMENT |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.06 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 134989 |
 ムービー
ムービー コントローラー
コントローラー







