+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-20818 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of HIV-1 neutralizing antibody DH270.6 in complex with CH848 10.17DT Env | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell /  viral protein processing / virus-mediated perturbation of host defense response / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral protein processing / virus-mediated perturbation of host defense response / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane /  エンベロープ (ウイルス) ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / エンベロープ (ウイルス) ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / positive regulation of establishment of T cell polarity / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell /  viral protein processing / virus-mediated perturbation of host defense response / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral protein processing / virus-mediated perturbation of host defense response / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane /  エンベロープ (ウイルス) / virion attachment to host cell / host cell plasma membrane / virion membrane / structural molecule activity / エンベロープ (ウイルス) / virion attachment to host cell / host cell plasma membrane / virion membrane / structural molecule activity /  細胞膜 細胞膜類似検索 - 分子機能 | |||||||||
| 生物種 |    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) / Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) /   Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 4.3 Å クライオ電子顕微鏡法 / 解像度: 4.3 Å | |||||||||
 データ登録者 データ登録者 | Acharya P / Henderson RC / Saunder KO / Haynes BF | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2019 ジャーナル: Science / 年: 2019タイトル: Targeted selection of HIV-specific antibody mutations by engineering B cell maturation. 著者: Kevin O Saunders / Kevin Wiehe / Ming Tian / Priyamvada Acharya / Todd Bradley / S Munir Alam / Eden P Go / Richard Scearce / Laura Sutherland / Rory Henderson / Allen L Hsu / Mario J Borgnia ...著者: Kevin O Saunders / Kevin Wiehe / Ming Tian / Priyamvada Acharya / Todd Bradley / S Munir Alam / Eden P Go / Richard Scearce / Laura Sutherland / Rory Henderson / Allen L Hsu / Mario J Borgnia / Haiyan Chen / Xiaozhi Lu / Nelson R Wu / Brian Watts / Chuancang Jiang / David Easterhoff / Hwei-Ling Cheng / Kelly McGovern / Peyton Waddicor / Aimee Chapdelaine-Williams / Amanda Eaton / Jinsong Zhang / Wes Rountree / Laurent Verkoczy / Mark Tomai / Mark G Lewis / Heather R Desaire / Robert J Edwards / Derek W Cain / Mattia Bonsignori / David Montefiori / Frederick W Alt / Barton F Haynes /  要旨: INTRODUCTION: A major goal of HIV-1 vaccine development is the design of immunogens that induce broadly neutralizing antibodies (bnAbs). However, vaccination of humans has not resulted in the ...INTRODUCTION: A major goal of HIV-1 vaccine development is the design of immunogens that induce broadly neutralizing antibodies (bnAbs). However, vaccination of humans has not resulted in the induction of affinity-matured and potent HIV-1 bnAbs. To devise effective vaccine strategies, we previously determined the maturation pathway of select HIV-1 bnAbs from acute infection through neutralizing antibody development. During their evolution, bnAbs acquire an abundance of improbable amino acid substitutions as a result of nucleotide mutations at variable region sequences rarely targeted by activation-induced cytidine deaminase, the enzyme responsible for antibody mutation. A subset of improbable mutations is essential for broad neutralization activity, and their acquisition represents a key roadblock to bnAb development. RATIONALE: Current bnAb lineage-based vaccine strategies can initiate bnAb lineage development in animal models but have not specifically elicited the improbable mutations required for neutralization ...RATIONALE: Current bnAb lineage-based vaccine strategies can initiate bnAb lineage development in animal models but have not specifically elicited the improbable mutations required for neutralization breadth. Induction of bnAbs requires vaccine strategies that specifically engage bnAb precursors and subsequently select for improbable mutations required for broadly neutralizing activity. We hypothesized that vaccination with immunogens that bind with moderate to high affinity to bnAb B cell precursors, and with higher affinity to precursors that have acquired improbable mutations, could initiate bnAb B cell lineages and select for key improbable mutations required for bnAb development. RESULTS: We elicited serum neutralizing HIV-1 antibodies in human bnAb precursor knock-in mice and wild-type macaques vaccinated with immunogens designed to select for improbable mutations. We ...RESULTS: We elicited serum neutralizing HIV-1 antibodies in human bnAb precursor knock-in mice and wild-type macaques vaccinated with immunogens designed to select for improbable mutations. We designed two HIV-1 envelope immunogens that bound precursor B cells of either a CD4 binding site or V3-glycan bnAb lineage. In vitro, these immunogens bound more strongly to bnAb precursors once the precursor acquired the desired improbable mutations. Vaccination of macaques with the CD4 binding site–targeting immunogen induced CD4 binding site serum neutralizing antibodies. Antibody sequences elicited in human bnAb precursor knock-in mice encoded functional improbable mutations critical for bnAb development. In bnAb precursor knock-in mice, we isolated a vaccine-elicited monoclonal antibody bearing functional improbable mutations that was capable of neutralizing multiple HIV-1 global isolates. Structures of a bnAb precursor, a bnAb, and the vaccine-elicited antibody revealed the precise roles that acquired improbable mutations played in recognizing the HIV-1 envelope. Thus, our immunogens elicited antibody responses in macaques and knock-in mice that exhibited the mutational patterns, structural characteristics, or neutralization profiles of nascent broadly neutralizing antibodies. CONCLUSION: Our study represents a proof of concept for targeted selection of improbable mutations to guide antibody affinity maturation. Moreover, this study demonstrates a rational strategy for ...CONCLUSION: Our study represents a proof of concept for targeted selection of improbable mutations to guide antibody affinity maturation. Moreover, this study demonstrates a rational strategy for sequential immunogen design to circumvent the difficult roadblocks in HIV-1 bnAb induction by vaccination. We show that immunogens should exhibit differences in affinity across antibody maturation stages where improbable mutations are necessary for the desired antibody function. This strategy of selection of specific antibody nucleotides by immunogen design can be applied to B cell lineages targeting other pathogens where guided affinity maturation is needed for a protective antibody response. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_20818.map.gz emd_20818.map.gz | 117.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-20818-v30.xml emd-20818-v30.xml emd-20818.xml emd-20818.xml | 15.3 KB 15.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_20818.png emd_20818.png | 118.6 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-20818 http://ftp.pdbj.org/pub/emdb/structures/EMD-20818 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20818 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-20818 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_20818.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_20818.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.08 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Complex of antibody DH270.6 with HIV-1 Env CH848 10.17DT
| 全体 | 名称: Complex of antibody DH270.6 with HIV-1 Env CH848 10.17DT |
|---|---|
| 要素 |
|
-超分子 #1: Complex of antibody DH270.6 with HIV-1 Env CH848 10.17DT
| 超分子 | 名称: Complex of antibody DH270.6 with HIV-1 Env CH848 10.17DT タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #2-#4, #1 |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 実験値: 360 KDa |
-分子 #1: CH848 10.17DT gp120
| 分子 | 名称: CH848 10.17DT gp120 / タイプ: protein_or_peptide / ID: 1 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 51.736535 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: AENLWVTVYY GVPVWKEAKT TLFCASDARA YEKEVHNVWA THACVPTDPS PQELVLGNVT ENFNMWKNDM VDQMHEDIIS LWDQSLKPC VKLTPLCVTL ICSDATVKTG TVEEMKNCSF NTTTEIRDKE KKEYALFYKP DIVPLSETNN TSEYRLINCN T SACTQACP ...文字列: AENLWVTVYY GVPVWKEAKT TLFCASDARA YEKEVHNVWA THACVPTDPS PQELVLGNVT ENFNMWKNDM VDQMHEDIIS LWDQSLKPC VKLTPLCVTL ICSDATVKTG TVEEMKNCSF NTTTEIRDKE KKEYALFYKP DIVPLSETNN TSEYRLINCN T SACTQACP KVTFEPIPIH YCAPAGYAIL KCNDETFNGT GPCSNVSTVQ CTHGIRPVVS TQLLLNGSLA EKEIVIRSEN LT NNAKIII VHLHTPVEIV CTRPNNNTRK SVRIGPGQTF YATGDIIGDI KQAHCNISEE KWNDTLQKVG IELQKHFPNK TIK YNQSAG GDMEITTHSF NCGGEFFYCN TSNLFNGTYN GTYISTNSSA NSTSTITLQC RIKQIINMWQ GVGRCMYAPP IAGN ITCRS NITGLLLTRD GGTNSNETET FRPAGGDMRD NWRSELYKYK VVKIEPLGVA PTRCKRRV |
-分子 #2: CH848 10.17DT gp41
| 分子 | 名称: CH848 10.17DT gp41 / タイプ: protein_or_peptide / ID: 2 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:    Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
| 分子量 | 理論値: 18.24583 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: VGRRRRRRAV GIGAVFLGFL GAAGSTMGAA SMTLTVQARN LLSGIVQQQS NLLRAPEAQQ HLLKLTVWGI KQLQARVLAV ERYLRDQQL LGIWGCSGKL ICCTNVPWNS SWSNRNLSEI WDNMTWLQWD KEISNYTQII YGLLEESQNQ QEKNEQDLLA L D |
-分子 #3: DH270.6 Heavy chain
| 分子 | 名称: DH270.6 Heavy chain / タイプ: protein_or_peptide / ID: 3 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 25.895893 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QVQLVQSGAQ MKNPGASVKV SCAPSGYTFT DFYIHWLRQA PGQGLQWMGW MNPQTGRTNT ARNFQGRVTM TRDTSIGTAY MELRSLTSD DTAIYYCTTG GWISLYYDSS YYPNFDHWGQ GTLLTVSGAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW ...文字列: QVQLVQSGAQ MKNPGASVKV SCAPSGYTFT DFYIHWLRQA PGQGLQWMGW MNPQTGRTNT ARNFQGRVTM TRDTSIGTAY MELRSLTSD DTAIYYCTTG GWISLYYDSS YYPNFDHWGQ GTLLTVSGAS TKGPSVFPLA PSSKSTSGGT AALGCLVKDY F PEPVTVSW NSGALTSGVH TFPAVLQSSG LYSLSSVVTV PSSSLGTQTY ICNVNHKPSN TKVDKRVEPK SCDKHHHHHH |
-分子 #4: DH270.6 Light chain
| 分子 | 名称: DH270.6 Light chain / タイプ: protein_or_peptide / ID: 4 / コピー数: 3 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 22.783273 KDa |
| 組換発現 | 生物種:   Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 配列 | 文字列: QSALTQPASV SGSPGQSITI SCTGTKYDVG SHDLVSWYQQ YPGKVPKYMI YEVNKRPSGV SNRFSGSKSG NTASLTISGL RAEDEADYY CCSFGGSATV VCGGGTKVTV LGQPKGAPSV TLFPPSSEEL QANKATLVCL ISDFYPGAVT VAWKADSSPV K AGVETTTP ...文字列: QSALTQPASV SGSPGQSITI SCTGTKYDVG SHDLVSWYQQ YPGKVPKYMI YEVNKRPSGV SNRFSGSKSG NTASLTISGL RAEDEADYY CCSFGGSATV VCGGGTKVTV LGQPKGAPSV TLFPPSSEEL QANKATLVCL ISDFYPGAVT VAWKADSSPV K AGVETTTP SKQSNNKYAA SSYLSLTPEQ WKSHRSYSCQ VTHEGSTVEK TVAPTECS |
-分子 #10: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 10 / コピー数: 18 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information | 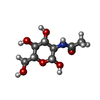 ChemComp-NAG: |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.2 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD Bright-field microscopy Bright-field microscopy |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 平均電子線量: 42.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
|---|---|
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 想定した対称性 - 点群: C3 (3回回転対称 ) / 解像度のタイプ: BY AUTHOR / 解像度: 4.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 107646 ) / 解像度のタイプ: BY AUTHOR / 解像度: 4.3 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 107646 |
 ムービー
ムービー コントローラー
コントローラー




















