+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of yeast CENP-OPQU+ bound to the CENP-A N-terminus | |||||||||||||||
 マップデータ マップデータ | ||||||||||||||||
 試料 試料 |
| |||||||||||||||
 キーワード キーワード |  kinetochore (動原体) / point centromere / CENP-A nucleosome / topological entrapment / centromeric DNA / kinetochore (動原体) / point centromere / CENP-A nucleosome / topological entrapment / centromeric DNA /  CELL CYCLE (細胞周期) CELL CYCLE (細胞周期) | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of meiotic DNA double-strand break formation involved in reciprocal meiotic recombination /  COMA complex / Mis6-Sim4 complex / centromere complex assembly / attachment of spindle microtubules to kinetochore / protein localization to chromosome, centromeric region / establishment of mitotic sister chromatid cohesion / COMA complex / Mis6-Sim4 complex / centromere complex assembly / attachment of spindle microtubules to kinetochore / protein localization to chromosome, centromeric region / establishment of mitotic sister chromatid cohesion /  spindle pole body / protein localization to kinetochore / mitotic spindle assembly checkpoint signaling ...negative regulation of meiotic DNA double-strand break formation involved in reciprocal meiotic recombination / spindle pole body / protein localization to kinetochore / mitotic spindle assembly checkpoint signaling ...negative regulation of meiotic DNA double-strand break formation involved in reciprocal meiotic recombination /  COMA complex / Mis6-Sim4 complex / centromere complex assembly / attachment of spindle microtubules to kinetochore / protein localization to chromosome, centromeric region / establishment of mitotic sister chromatid cohesion / COMA complex / Mis6-Sim4 complex / centromere complex assembly / attachment of spindle microtubules to kinetochore / protein localization to chromosome, centromeric region / establishment of mitotic sister chromatid cohesion /  spindle pole body / protein localization to kinetochore / mitotic spindle assembly checkpoint signaling / meiotic cell cycle / spindle pole body / protein localization to kinetochore / mitotic spindle assembly checkpoint signaling / meiotic cell cycle /  chromosome segregation / chromosome segregation /  動原体 / 動原体 /  細胞分裂 / 細胞分裂 /  細胞核 / 細胞核 /  細胞質 細胞質類似検索 - 分子機能 | |||||||||||||||
| 生物種 |   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) | |||||||||||||||
| 手法 |  単粒子再構成法 / 単粒子再構成法 /  クライオ電子顕微鏡法 / 解像度: 3.4 Å クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||||||||
 データ登録者 データ登録者 | Dendooven TD / Zhang Z / Yang J / McLaughlin S / Schwabb J / Scheres S / Yatskevich S | |||||||||||||||
| 資金援助 |  英国, 英国,  ドイツ, 4件 ドイツ, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Sci Adv / 年: 2023 ジャーナル: Sci Adv / 年: 2023タイトル: Cryo-EM structure of the complete inner kinetochore of the budding yeast point centromere. 著者: Tom Dendooven / Ziguo Zhang / Jing Yang / Stephen H McLaughlin / Johannes Schwab / Sjors H W Scheres / Stanislau Yatskevich / David Barford /  要旨: The point centromere of budding yeast specifies assembly of the large kinetochore complex to mediate chromatid segregation. Kinetochores comprise the centromere-associated inner kinetochore (CCAN) ...The point centromere of budding yeast specifies assembly of the large kinetochore complex to mediate chromatid segregation. Kinetochores comprise the centromere-associated inner kinetochore (CCAN) complex and the microtubule-binding outer kinetochore KNL1-MIS12-NDC80 (KMN) network. The budding yeast inner kinetochore also contains the DNA binding centromere-binding factor 1 (CBF1) and CBF3 complexes. We determined the cryo-electron microscopy structure of the yeast inner kinetochore assembled onto the centromere-specific centromere protein A nucleosomes (CENP-A). This revealed a central CENP-A with extensively unwrapped DNA ends. These free DNA duplexes bind two CCAN protomers, one of which entraps DNA topologically, positioned on the centromere DNA element I (CDEI) motif by CBF1. The two CCAN protomers are linked through CBF3 forming an arch-like configuration. With a structural mechanism for how CENP-A can also be linked to KMN involving only CENP-QU, we present a model for inner kinetochore assembly onto a point centromere and how it organizes the outer kinetochore for chromosome attachment to the mitotic spindle. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_17225.map.gz emd_17225.map.gz | 9.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-17225-v30.xml emd-17225-v30.xml emd-17225.xml emd-17225.xml | 20.7 KB 20.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_17225.png emd_17225.png | 48.3 KB | ||
| その他 |  emd_17225_half_map_1.map.gz emd_17225_half_map_1.map.gz emd_17225_half_map_2.map.gz emd_17225_half_map_2.map.gz | 17.4 MB 17.4 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-17225 http://ftp.pdbj.org/pub/emdb/structures/EMD-17225 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17225 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-17225 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_17225.map.gz / 形式: CCP4 / 大きさ: 18.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_17225.map.gz / 形式: CCP4 / 大きさ: 18.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.652 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-ハーフマップ: #1
| ファイル | emd_17225_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
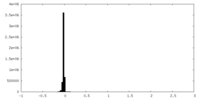
| 投影像・断面図 |
| ||||||||||||
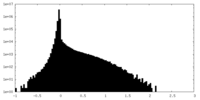
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_17225_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : A complex of CBF1-CCAN bound to centromeric C0N3 DNA
| 全体 | 名称: A complex of CBF1-CCAN bound to centromeric C0N3 DNA |
|---|---|
| 要素 |
|
-超分子 #1: A complex of CBF1-CCAN bound to centromeric C0N3 DNA
| 超分子 | 名称: A complex of CBF1-CCAN bound to centromeric C0N3 DNA タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: all |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
-分子 #1: Inner kinetochore subunit MCM21
| 分子 | 名称: Inner kinetochore subunit MCM21 / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 43.028879 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MSRIDDLQQD IESLLSEINS LEESREKLKA KIKDKRKNEE SANPIVQEFE DLFDQFPQLN NFLFNEHPEL EETDDKDISR AQADIPATP IPYEPKKRAK LENEEILPEQ EWVLKTQPMV QHQMFDPGVA DLLDTDILTS PSKRKRKLKI DDISTSDRSE L EDYIVLEN ...文字列: MSRIDDLQQD IESLLSEINS LEESREKLKA KIKDKRKNEE SANPIVQEFE DLFDQFPQLN NFLFNEHPEL EETDDKDISR AQADIPATP IPYEPKKRAK LENEEILPEQ EWVLKTQPMV QHQMFDPGVA DLLDTDILTS PSKRKRKLKI DDISTSDRSE L EDYIVLEN VYRMFGITFF PLVDPIDLKI KDASGEIFVD REMLGIRLEV FSERTSQFEK PHYVLLKKRI KSNSWFLFKH TI PSFIDVQ GIFDDTNGGL VISHDDAYLF AKRVFLQLVE VQKRRQIFKD LEAKKIIHDL DLDLESSMVS FFVKDIKVEL FVK QNEIVS CSILDDIHDF SQNNKSKWEI ALLGSLDDLE LKLNHSFATI FK UniProtKB: Inner kinetochore subunit MCM21 |
-分子 #2: Inner kinetochore subunit CTF19
| 分子 | 名称: Inner kinetochore subunit CTF19 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 42.841113 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MDFTSDTTNS HDTSNSHLSL EDAVGTHHAG EADVNIDGDE KQQLSLLDDD QVRALKLQEE KDALLTRRNT LLQEIQTYQN ILMKENNSK TKNGDILQND ITQDFLNLIS ISSSNPNSAI SDRKRVERIN GLTNLQKELV TKYDTLPLLN MNLRLSYLRD H TYPHLQVS ...文字列: MDFTSDTTNS HDTSNSHLSL EDAVGTHHAG EADVNIDGDE KQQLSLLDDD QVRALKLQEE KDALLTRRNT LLQEIQTYQN ILMKENNSK TKNGDILQND ITQDFLNLIS ISSSNPNSAI SDRKRVERIN GLTNLQKELV TKYDTLPLLN MNLRLSYLRD H TYPHLQVS VQSRDRVHND GIEVLVVNYK FCRNTMNPFE IQFKMFYKFE DSTLLKWEIL RISTNVRLKA KQLLATRNFQ KC LLSLYEF DKIKSKKTGI FQNLINLLKR KTRCYLMNNS DSLIVERVIR EGRLTTIKLQ INFIITMPGE RGKPRNCFLP MSK ISIALW KGGERFNQID LDEICYGLIK EYGVKTGLKE ICNVCLFPDM YAR UniProtKB: Inner kinetochore subunit CTF19 |
-分子 #3: Inner kinetochore subunit OKP1
| 分子 | 名称: Inner kinetochore subunit OKP1 / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 47.427246 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MAADRDNFLQ NIENDSINNG QAMDLSPNRS SSESDSSILM NVNDIKTLRL DVAPEAKSTQ SKKSLFYENS DDAEEGEIEE RTNKEEGQY HHKGSKQLRF EVGKESTGKL QSHLSDGSAT SGEGNVRPWE FRKVIQAEYR ERLPRNYELK HWKKPSKIMI G SILRLLET ...文字列: MAADRDNFLQ NIENDSINNG QAMDLSPNRS SSESDSSILM NVNDIKTLRL DVAPEAKSTQ SKKSLFYENS DDAEEGEIEE RTNKEEGQY HHKGSKQLRF EVGKESTGKL QSHLSDGSAT SGEGNVRPWE FRKVIQAEYR ERLPRNYELK HWKKPSKIMI G SILRLLET NTVSALDSVF EKYEKEMNQM THGDNNEVKR IYSKKERLLE IILTKIKKKL RQAKFPSRIS ERDLDIEYIY SK RQFIQNR YSQELQNNER LEAILSREQN LLEETRKLCM NLKTNNKKRL TEKLIQKDLH PVLNKAMEYT YGLESTNGFM HPD GPVTFR NDSHELNLML NDPIKSTADV RLDKEEVLSL LPSLKEYTKK SKELKETMGQ MISDSHEEEI KEVFVPHHES HQDK TEEDI H UniProtKB: Inner kinetochore subunit OKP1 |
-分子 #4: Inner kinetochore subunit AME1
| 分子 | 名称: Inner kinetochore subunit AME1 / タイプ: protein_or_peptide / ID: 4 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 37.506723 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MDRDTKLAFR LRGSHSRRTD DIDDDVIVFK TPNAVYREEN SPIQSPVQPI LSSPKLANSF EFPITTNNVN AQDRHEHGYQ PLDAEDYPM IDSENKSLIS ESPQNVRNDE DLTTRYNFDD IPIRQLSSSI TSVTTIDVLS SLFINLFEND LIPQALKDFN K SDDDQFRK ...文字列: MDRDTKLAFR LRGSHSRRTD DIDDDVIVFK TPNAVYREEN SPIQSPVQPI LSSPKLANSF EFPITTNNVN AQDRHEHGYQ PLDAEDYPM IDSENKSLIS ESPQNVRNDE DLTTRYNFDD IPIRQLSSSI TSVTTIDVLS SLFINLFEND LIPQALKDFN K SDDDQFRK LLYKLDLRLF QTISDQMTRD LKDILDINVS NNELCYQLKQ VLARKEDLNQ QIISVRNEIQ ELKAGKDWHD LQ NEQAKLN DKVKLNKRLN DLTSTLLGKY EGDRKIMSQD SEDDSIRDDS NILDIAHFVD LMDPYNGLLK KINKINENLS NEL QPSL UniProtKB: Inner kinetochore subunit AME1 |
-分子 #5: Inner kinetochore subunit NKP1
| 分子 | 名称: Inner kinetochore subunit NKP1 / タイプ: protein_or_peptide / ID: 5 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 27.006451 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MTDTYNSISN FIENELTALL SSDDYLMDDL AGELPNEVCR LLKAQVIEKR KDAMSRGKQD LLSKEIYDNE SELRASQSQQ IMELVGDIP KYSLGSELRN RVEGEPQSTS IERLIEDVLK LPQMEVADEE EVEVENDLKV LSEYSNLRKD LILKCQALQI G ESKLSDIL ...文字列: MTDTYNSISN FIENELTALL SSDDYLMDDL AGELPNEVCR LLKAQVIEKR KDAMSRGKQD LLSKEIYDNE SELRASQSQQ IMELVGDIP KYSLGSELRN RVEGEPQSTS IERLIEDVLK LPQMEVADEE EVEVENDLKV LSEYSNLRKD LILKCQALQI G ESKLSDIL SQTNSINSLT TSIKEASEDD DISEYFATYN GKLVVALEEM KLLLEEAVKT FGNSPEKREK IKKILSELKK UniProtKB: Inner kinetochore subunit NKP1 |
-分子 #6: Inner kinetochore subunit NKP2
| 分子 | 名称: Inner kinetochore subunit NKP2 / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:   Saccharomyces cerevisiae (パン酵母) Saccharomyces cerevisiae (パン酵母) |
| 分子量 | 理論値: 17.877033 KDa |
| 組換発現 | 生物種:   Trichoplusia ni (イラクサキンウワバ) Trichoplusia ni (イラクサキンウワバ) |
| 配列 | 文字列: MNSEQLLHNY VSDSLLTTLI SFQEFKQQLQ SYTSDEQQLQ HWYELLQARD ARVTSELEAR IKQFFITLRS RLLRFLESEQ LSHSLSLET LIDALYKIND LLQQRLQILD DAIQEKTSEL AEFENMVRSP SAGDNAIPGL LQIIQSYINL LEEN UniProtKB: Inner kinetochore subunit NKP2 |
-実験情報
-構造解析
| 手法 |  クライオ電子顕微鏡法 クライオ電子顕微鏡法 |
|---|---|
 解析 解析 |  単粒子再構成法 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD Bright-field microscopy / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 1.0 µm Bright-field microscopy / 最大 デフォーカス(公称値): 2.6 µm / 最小 デフォーカス(公称値): 1.0 µm |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 平均電子線量: 40.0 e/Å2 |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: NONE |
|---|---|
| 初期 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 角度割当 | タイプ: MAXIMUM LIKELIHOOD |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.4 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 595147 |
 ムービー
ムービー コントローラー
コントローラー
















 Z
Z Y
Y X
X