+検索条件
-Structure paper
| タイトル | De novo design of proteins housing excitonically coupled chlorophyll special pairs. |
|---|---|
| ジャーナル・号・ページ | Nat Chem Biol, Year 2024 |
| 掲載日 | 2024年6月3日 |
 著者 著者 | Nathan M Ennist / Shunzhi Wang / Madison A Kennedy / Mariano Curti / George A Sutherland / Cvetelin Vasilev / Rachel L Redler / Valentin Maffeis / Saeed Shareef / Anthony V Sica / Ash Sueh Hua / Arundhati P Deshmukh / Adam P Moyer / Derrick R Hicks / Avi Z Swartz / Ralph A Cacho / Nathan Novy / Asim K Bera / Alex Kang / Banumathi Sankaran / Matthew P Johnson / Amala Phadkule / Mike Reppert / Damian Ekiert / Gira Bhabha / Lance Stewart / Justin R Caram / Barry L Stoddard / Elisabet Romero / C Neil Hunter / David Baker /    |
| PubMed 要旨 | Natural photosystems couple light harvesting to charge separation using a 'special pair' of chlorophyll molecules that accepts excitation energy from the antenna and initiates an electron-transfer ...Natural photosystems couple light harvesting to charge separation using a 'special pair' of chlorophyll molecules that accepts excitation energy from the antenna and initiates an electron-transfer cascade. To investigate the photophysics of special pairs independently of the complexities of native photosynthetic proteins, and as a first step toward creating synthetic photosystems for new energy conversion technologies, we designed C-symmetric proteins that hold two chlorophyll molecules in closely juxtaposed arrangements. X-ray crystallography confirmed that one designed protein binds two chlorophylls in the same orientation as native special pairs, whereas a second designed protein positions them in a previously unseen geometry. Spectroscopy revealed that the chlorophylls are excitonically coupled, and fluorescence lifetime imaging demonstrated energy transfer. The cryo-electron microscopy structure of a designed 24-chlorophyll octahedral nanocage with a special pair on each edge closely matched the design model. The results suggest that the de novo design of artificial photosynthetic systems is within reach of current computational methods. |
 リンク リンク |  Nat Chem Biol / Nat Chem Biol /  PubMed:38831036 PubMed:38831036 |
| 手法 | EM (単粒子) / X線回折 |
| 解像度 | 2 - 6.5 Å |
| 構造データ | EMDB-40208, PDB-8glt:  EMDB-40209: Chlorophyll-binding region of de novo-designed nanocage O32-15  PDB-7unh:  PDB-7uni:  PDB-7unj:  PDB-8evm: |
| 化合物 | 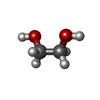 ChemComp-EDO:  ChemComp-HOH:  ChemComp-OE9: 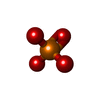 ChemComp-PO4: 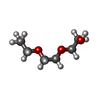 ChemComp-PGE: 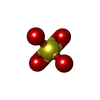 ChemComp-SO4: |
| 由来 |
|
 キーワード キーワード |  DE NOVO PROTEIN (De novo) / DE NOVO PROTEIN (De novo) /  design (デザイン) / design (デザイン) /  homodimer / rosetta / homodimer / rosetta /  symmetric (対称性) / symmetric (対称性) /  designed (デザイン) / circular tandem repeat protein / cTRP / apo / designed (デザイン) / circular tandem repeat protein / cTRP / apo /  chlorophyll (クロロフィル) / Zn pheophorbide a methyl ester / Zn / de novo design / chlorophyll (クロロフィル) / Zn pheophorbide a methyl ester / Zn / de novo design /  electron donor / electron donor /  photosynthetic (光合成) / photosynthetic (光合成) /  nanocage / helical repeats / chlorophyll-binding / nanocage / helical repeats / chlorophyll-binding /  octahedral symmetry octahedral symmetry |
 ムービー
ムービー コントローラー
コントローラー 構造ビューア
構造ビューア 万見文献について
万見文献について





